2026年4月3日,复旦大学人类表型组研究院钱斌治教授联合类脑智能科学与技术研究院原致远研究员在国际期刊《Nature Computational Science》上发表题为Benchmarking Alignment Methods for Spatial Transcriptomics Data的研究论文。该研究围绕空间转录组对齐问题,在多种应用场景下对现有方法进行了系统且多维度的评估,并为方法选择与开发提供了具有指导意义的参考框架。

随着空间转录组技术的快速发展,研究者能够在组织原位解析分子的分布特征,进一步加深了对相关生物学问题的理解。目前多数平台仍以二维切片为主要数据形式,因此,如何实现二维切片之间的高精度配准并重建统一的三维空间坐标,进而促进对复杂生物组织三维构型的系统性解析已成为空间组学领域亟需解决的重要问题之一。该任务在生物医学研究中具有重要价值,然而,空间转录组数据通常具有表达高度稀疏、跨平台差异显著等特征,并叠加组织形变、旋转等因素,进一步加剧了对齐任务的难度。近年来相关方法不断涌现,但针对多场景、多数据类型的系统性评估仍相对匮乏。因此,构建覆盖多平台、多组织类型及多应用情境的标准化评测体系,对于全面厘清各类方法的性能边界、辅助用户选择与应用,并进一步推动方法学发展具有重要意义。
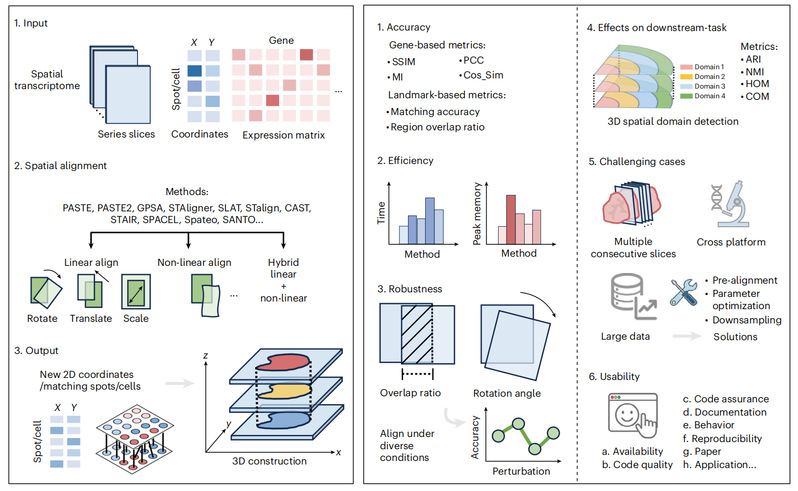
研究首先建立了一套系统化的方法评测框架,对11种代表性空间对齐算法在多种任务场景下进行了统一评估,并从多个维度对其性能进行了量化分析。框架整体可分为以下几个部分:对齐精度评估、计算效率分析、方法鲁棒性测试、对下游任务影响的评估、复杂挑战场景下的性能测试,以及用户指南的构建。在此基础上,进一步探究性能差异的潜在机制,并提出对下一代方法开发的启示。
在对齐性能方面,除直观的可视化比较外,构建了基于表达与注释标签匹配的双重定量评估体系。对于具备真实三维空间参考坐标的数据,进一步引入平均绝对误差等指标。同时,通过对运行时间与峰值内存占用的统计,对不同方法的计算开销及潜在瓶颈进行了分析。综合结果显示,各类方法的性能表现与数据特征密切相关,因此在实际应用中需在精度、效率及适用性之间进行权衡。
在稳定性层面,研究通过构建扰动实验体系(包括切片重叠比例变化与初始旋转偏移),系统评估了方法在不同初始条件下的鲁棒性。结果表明,各方法对初始状态的依赖程度差异显著:部分方法对初始位置高度敏感,而部分方法则能够在扰动条件下保持较为稳定的性能。此外,分析进一步指出,粗配准步骤在整体流程中具有关键性作用,对最终对齐质量产生重要影响。
在应用价值方面,研究将对齐结果引入三维空间域识别等下游分析任务,并以ARI与NMI等经典指标进行评估。结果表明,在多数测试场景中,更高精度的对齐能够显著提升下游分析表现,从而验证了高质量配准在实际生物学研究中的重要意义。
进一步地,为贴近真实应用需求,研究模拟了多类复杂挑战性场景,包括连续多切片对齐、跨技术平台及大规模数据等。评估发现,现有方法在上述情境下普遍面临性能退化与资源消耗显著增加的问题。针对这些挑战,研究提出了一系列可灵活组合的策略,为大规模数据的对齐提供了可行解决思路。综合上述结果,研究提出对齐用户指南,涵盖数据预处理、方法选择、对齐执行及结果评估等关键环节。
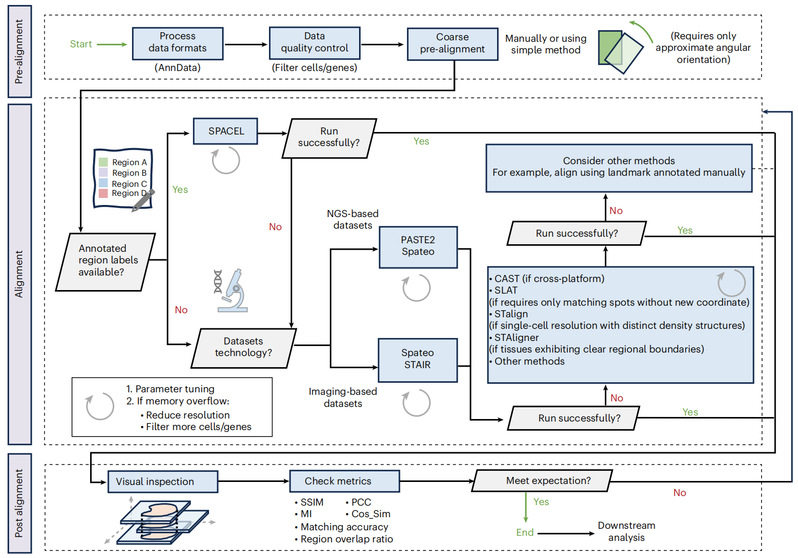
除了评估本身,研究还进一步对影响对齐效果的关键因素进行探索,并分析不同方法性能差异产生的潜在机制,为下一代空间对齐算法的设计与优化提供了重要启示。
复旦大学钱斌治教授和原致远研究员为本文通讯作者。复旦大学博士生严筠芷为本文第一作者。感谢所有合作者对本文的支持与帮助。
原文链接:https://www.nature.com/articles/s43588-026-00977-z






